对于有很多(成百上千)研究对象时,把对象分组是最常用的研究手段。而通过观察值进行聚类是非常有效的方法,可以按事物观察值有效的合理分组,再进一步分析各组的相同、与不同,可以很好的发现其中的规律。
本文将带你学习在R语言的Rstudio环境中,使用cluster、facteoextra包,以及kmeans进分析最优分组、评估及可视化。
准备包和数据
- # 清空环境
- rm(list=ls())
- # 安装包并加载包
- # 使用k-means聚类所需的包:factoextra和cluster
- site="https://mirrors.tuna.tsinghua.edu.cn/CRAN"
- package_list = c("factoextra","cluster")
- for(p in package_list){
- if(!suppressWarnings(suppressMessages(require(p, character.only = TRUE, quietly = TRUE, warn.conflicts = FALSE)))){
- install.packages(p, repos=site)
- suppressWarnings(suppressMessages(library(p, character.only = TRUE, quietly = TRUE, warn.conflicts = FALSE)))
- }
- }
- # 数据准备
- # 使用内置的R数据集USArrests
- data("USArrests")
- # remove any missing value (i.e, NA values for not available)
- USArrests = na.omit(USArrests) #view the first 6 rows of the data
- head(USArrests, n=6)
- # 显示测试数据示例如下
在此数据集中,列是变量,行是观测值。显示测试数据示例如下:
- Murder Assault UrbanPop Rape
- Alabama 13.2 236 58 21.2
- Alaska 10.0 263 48 44.5
- Arizona 8.1 294 80 31.0
- Arkansas 8.8 190 50 19.5
- California 9.0 276 91 40.6
- Colorado 7.9 204 78 38.7
数据基本统计
在聚类之前我们可以先进行一些必要的数据检查即数据描述性统计,如平均值、标准差等
- # 在聚类之前我们可以先进行一些必要的数据检查即数据描述性统计,如平均值、标准差等
- desc_stats = data.frame( Min=apply(USArrests, 2, min),#minimum
- Med=apply(USArrests, 2, median),#median
- Mean=apply(USArrests, 2, mean),#mean
- SD=apply(USArrests, 2, sd),#Standard deviation
- Max=apply(USArrests, 2, max)#maximum
- )
- desc_stats = round(desc_stats, 1)#保留小数点后一位head(desc_stats)
- desc_stats
统计结果如下:
- Min Med Mean SD Max
- Murder 0.8 7.2 7.8 4.4 17.4
- Assault 45.0 159.0 170.8 83.3 337.0
- UrbanPop 32.0 66.0 65.5 14.5 91.0
- Rape 7.3 20.1 21.2 9.4 46.0
数据标准化和评估
- # 变量有很大的方差及均值时需进行标准化
- df = scale(USArrests)
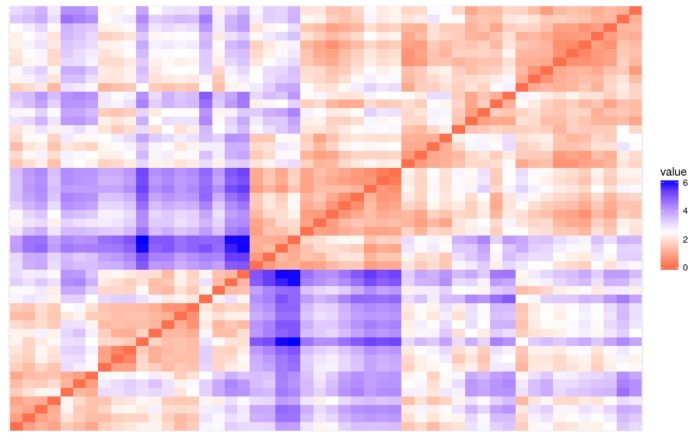
- # 数据集群性评估,使用get_clust_tendency()计算Hopkins统计量
- res = get_clust_tendency(df, 40, graph = TRUE)
- res$hopkins_stat
- [1] 0.344087
Hopkins统计量的值<0.5,表明数据是高度可聚合的。
- res$plot
另外,从图中也可以看出数据可聚合。
估计聚合簇数
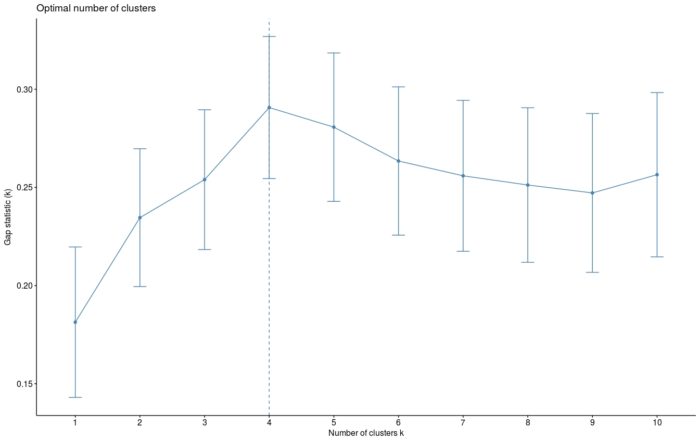
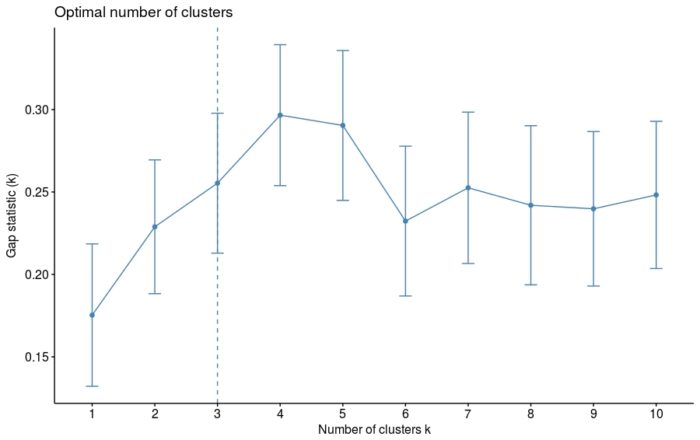
由于k均值聚类需要指定要生成的聚类数量,因此我们将使用函数clusGap()来计算用于估计最优聚类数。函数fviz_gap_stat()用于可视化。
- set.seed(123)
- ## Compute the gap statistic
- gap_stat = clusGap(df, FUN = kmeans, nstart = 25, K.max = 10, B = 500)
- # Plot the result
- fviz_gap_stat(gap_stat)
图中显示最佳为聚成四类(k=4)
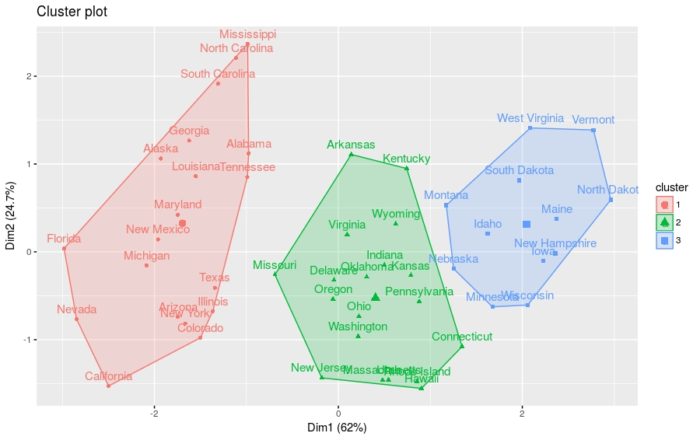
kmeans进行聚类
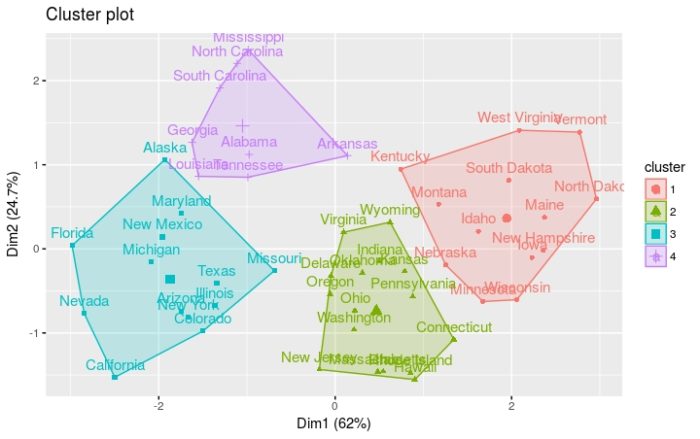
kmeans按四组进行聚类,选择25个随机集
- km.res = kmeans(df, 4, nstart = 25)
- # Visualize clusters using factoextra
- fviz_cluster(km.res, USArrests)
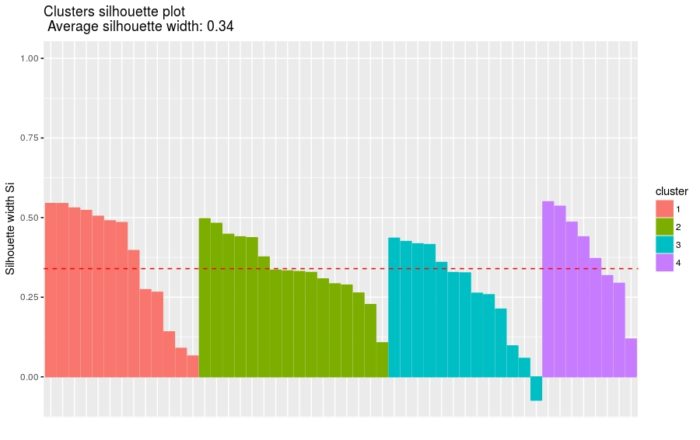
提取聚类轮廓图
- sil = silhouette(km.res$cluster, dist(df))
- rownames(sil) = rownames(USArrests)
- head(sil[, 1:3])
四个cluster的基本信息
- cluster size ave.sil.width
- 1 1 13 0.37
- 2 2 16 0.34
- 3 3 13 0.27
- 4 4 8 0.39
可视化
- # Visualize
- fviz_silhouette(sil)
图片尺寸宽900 dpi较适合微信手机端阅读
图中可以看出有负值,可以通过函数silhouette()确定是哪个观测值
- neg_sil_index = which(sil[, "sil_width"] < 0)
- sil[neg_sil_index, , drop = FALSE]
显示为负的观测值
- cluster neighbor sil_width
- Missouri 3 2 -0.07318144
eclust():增强的聚类分析
与其他聚类分析包相比,eclust()有以下优点: 简化了聚类分析的工作流程,可以用于计算层次聚类和分区聚类,eclust()自动计算最佳聚类簇数。 自动提供Silhouette plot,可以结合ggplot2绘制优美的图形,使用eclust()的K均值聚类
- # Compute k-means
- res.km = eclust(df, "kmeans")
- # Gap statistic plot
- fviz_gap_stat(res.km$gap_stat)
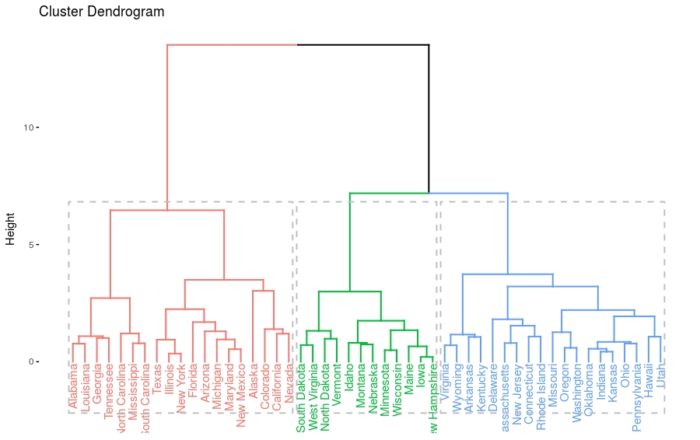
使用eclust()的层次聚类
- # Enhanced hierarchical clustering
- res.hc = eclust(df, "hclust") # compute hclust
- fviz_dend(res.hc, rect = TRUE) # dendrogam
层级聚类结果
下面的R代码生成Silhouette plot和分层聚类散点图。
- fviz_silhouette(res.hc) # silhouette plot
- fviz_cluster(res.hc) # scatter plot
R分析环境相关信息
- sessionInfo()
- R version 3.4.1 (2017-06-30)
- Platform: x86_64-pc-linux-gnu (64-bit)
- Running under: Ubuntu 16.04.3 LTS
- Matrix products: default
- BLAS: /usr/lib/openblas-base/libblas.so.3
- LAPACK: /usr/lib/libopenblasp-r0.2.18.so
- locale:
- [1] LC_CTYPE=en_US.UTF-8 LC_NUMERIC=C LC_TIME=en_US.UTF-8 LC_COLLATE=en_US.UTF-8 LC_MONETARY=en_US.UTF-8
- [6] LC_MESSAGES=en_US.UTF-8 LC_PAPER=en_US.UTF-8 LC_NAME=C LC_ADDRESS=C LC_TELEPHONE=C
- [11] LC_MEASUREMENT=en_US.UTF-8 LC_IDENTIFICATION=C
- attached base packages:
- [1] stats graphics grDevices utils datasets methods base
- other attached packages:
- [1] cluster_2.0.6 factoextra_1.0.5 ggplot2_2.2.1
- loaded via a namespace (and not attached):
- [1] Rcpp_0.12.15 DEoptimR_1.0-8 pillar_1.1.0 compiler_3.4.1 plyr_1.8.4 ggpubr_0.1.6.999 bindr_0.1
- [8] viridis_0.4.1 class_7.3-14 prabclus_2.2-6 tools_3.4.1 dendextend_1.6.0 digest_0.6.14 mclust_5.4
- [15] viridisLite_0.2.0 tibble_1.4.2 gtable_0.2.0 lattice_0.20-35 pkgconfig_2.0.1 rlang_0.1.6 ggrepel_0.7.0
- [22] yaml_2.1.16 mvtnorm_1.0-6 bindrcpp_0.2 gridExtra_2.3 trimcluster_0.1-2 dplyr_0.7.4 stringr_1.2.0
- [29] fpc_2.1-11 diptest_0.75-7 nnet_7.3-12 stats4_3.4.1 grid_3.4.1 robustbase_0.92-8 glue_1.2.0
- [36] R6_2.2.2 flexmix_2.3-14 kernlab_0.9-25 reshape2_1.4.3 purrr_0.2.4 magrittr_1.5 whisker_0.3-2
- [43] scales_0.5.0 modeltools_0.2-21 MASS_7.3-48 assertthat_0.2.0 colorspace_1.3-2 labeling_0.3 stringi_1.1.6
- [50] lazyeval_0.2.1 munsell_0.4.3