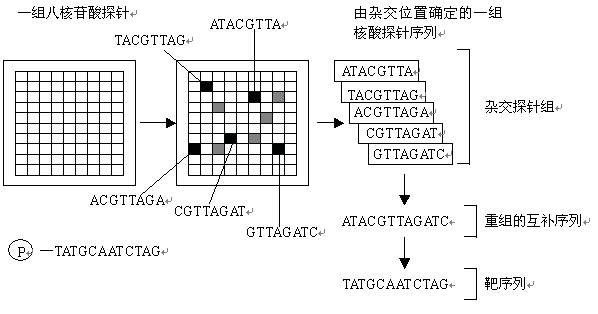
基因芯片(gene chip)的原型是80年代中期提出的。基因芯片的测序原理是杂交测序方法,即通过与一组已知序列的核酸探针杂交进行核酸序列测定的方法,可以用图11-5-1来说明。在一块基片表面固定了序列已知的八核苷酸的探针。当溶液中带有荧光标记的核酸序列TATGCAATCTAG,与基因芯片上对应位置的核酸探针产生互补匹配时,通过确定荧光强度最强的探针位置,获得一组序列完全互补的探针序列。据此可重组出靶核酸的序列。
- 基因芯片的测序原理图
基因芯片又称为DNA微阵列(DNA microarray),可分为三种主要类型:1)固定在聚合物基片(尼龙膜,硝酸纤维膜等)表面上的核酸探针或cDNA片段,通常用同位素标记的靶基因与其杂交,通过放射显影技术进行检测。这种方法的优点是所需检测设备与目前分子生物学所用的放射显影技术相一致,相对比较成熟。但芯片上探针密度不高,样品和试剂的需求量大,定量检测存在较多问题。2)用点样法固定在玻璃板上的DNA探针阵列,通过与荧光标记的靶基因杂交进行检测。这种方法点阵密度可有较大的提高,各个探针在表面上的结合量也比较一致,但在标准化和批量化生产方面仍有不易克服的困难。3)在玻璃等硬质表面上直接合成的寡核苷酸探针阵列,与荧光标记的靶基因杂交进行检测。该方法把微电子光刻技术与DNA化学合成技术相结合,可以使基因芯片的探针密度大大提高,减少试剂的用量,实现标准化和批量化大规模生产,有着十分重要的发展潜力。
- 基因芯片原型
它是在基因探针的基础上研制出的,所谓基因探针只是一段人工合成的碱基序列,在探针上连接一些可检测的物质,根据碱基互补的原理,利用基因探针到基因混合物中识别特定基因。它将大量探针分子固定于支持物上,然后与标记的样品进行杂交,通过检测杂交信号的强度及分布来进行分析。基因芯片通过应用平面微细加工技术和超分子自组装技术,把大量分子检测单元集成在一个微小的固体基片表面,可同时对大量的核酸和蛋白质等生物分子实现高效、快速、低成本的检测和分析。
由于尚未形成主流技术,生物芯片的形式非常多,以基质材料分,有尼龙膜、玻璃片、塑料、硅胶晶片、微型磁珠等;以所检测的生物信号种类分,有核酸、蛋白质、生物组织碎片甚至完整的活细胞;按工作原理分类,有杂交型、合成型、连接型、亲和识别型等。由于生物芯片概念是随着人类基因组的发展一起建立起来的,所以至今为止生物信号平行分析最成功的形式是以一种尼龙膜为基质的“cDNA阵列”,用于检测生物样品中基因表达谱的改变。



1F
x谢谢